Tuần tin khoa học 975 (12-18/01/2026)
GWAS phân lập được gen ứng cử viên điều khiển tập tính tăng trưởng đậu chickpea
Nguồn: Rajib Kumbhakar, Mayulika Mondal, Virevol Thakro, Yashwant K. Yadava, Uday Chand Jha, Shailesh Tripathi & Swarup K. Parida. 2026. A genome-wide association analysis identifies a key candidate gene controlling plant growth habit in chickpea. TAG; January 3 2026; vol. 139; article 22

![]() Tích hợp kết quả GWAS và phân tích haplotype đã xác định được một locus chủ chốt điều khiển tính trạng PHG (growth habit: tập tính tăng trưởng) của đậu chickpea.
Tích hợp kết quả GWAS và phân tích haplotype đã xác định được một locus chủ chốt điều khiển tính trạng PHG (growth habit: tập tính tăng trưởng) của đậu chickpea.
Xác định những markers phân tử cho tính trạng PHG này sẽ có thể giúp chúng ta biết được khả năng thu hoạch cơ giới; đây là nguyên tắc cơ bản của hiệu quả đột phá năng suất, sản lượng cây trồng trong điều kiện biến đổi khí hậu và gia tăng nhu cầu lương thực toàn cầu. Kết hợp chiến lược chọn giống nhờ GWAS thông qua bản đồ di truyền “association mapping” và kết quả phân tích association trên cơ sở “haplotype”, phương pháp “haplotyping” phân tử và kết quả phân tích biểu hiện gen của tập đoàn bao gồm 286 mẫu giống đậu chickpea (Cicer arietinum), người ta tìm ra cơ sở di truyền của các tính trạng liên quan đến PGH. Người ta ứng dụng 382.171 chỉ thị SNPs có từ WGS (whole-genome sequencing) của mẫu giống chickpea, đó là 286 loại hình desi và kabuli. Người ta khoanh vùng tại một locus chính có li6en quan đến biến thể của tính trạng PGH, đặc biệt là giữa kiểu hình mọc đứng : erect (E)/semi-erect (SE) so sánh với kiểu hình mọc bò: spreading (S)/semi-spreading (SS). Trong loci này, gen CaPAR1 (Cicer arietinum PAR1) và những alleles/haplotypes dẫn xuất tự nhiên của nó được xác định là gen ứng cử viên. Kết quả có thể giúp chúng ta sáng tạo nên giống mới cao sản, mọc đứng erect/semi-erect, giống cho phép thu hoạch cơ giới thông qua nghiên cứu genomics và chọn giống phân tử giống đậu chickpea.
Xem https://link.springer.com/article/10.1007/s00122-025-05121-5
Biến thể tự nhiên của gen MYC2 điều khiển tính kháng sâu xanh da láng của đậu nành
Nguồn: Xiao Li, Dezhou Hu, Zhongyi Yang, Linyan Cai, Mengshan Zhang, Hailun Liu, Dongquan Guo, Shupeng Dong, Changyun Yang, Fang Huang, Deyue Yu, and Hui Wang. 2025. A natural variant of an MYC2 gene in soybean contributes to resistance against the common cutworm. PNAS; December 26 2025; 122 (52) e2424956122; https://doi.org/10.1073/pnas.2424956122.
 Thực vật liên tục bị đe dọa bởi sâu ăn lá trong chu kỳ sinh trưởng. Với cây đậu nành, sâu phổ biến có tên là CCW (common cutworm) (sâu xanh da láng: Spodoptera litura) là đối tượng chính làm thiệt hại năng suất đáng kể trên nhiều vùng canh tác. Ví dụ, ở châu Á, sự xuất hiện của nó thường làm giảm năng suất hàng năm từ 10 đến 20%, với sự thất mùa hơn 50% khi dịch hại bùng phát.
Thực vật liên tục bị đe dọa bởi sâu ăn lá trong chu kỳ sinh trưởng. Với cây đậu nành, sâu phổ biến có tên là CCW (common cutworm) (sâu xanh da láng: Spodoptera litura) là đối tượng chính làm thiệt hại năng suất đáng kể trên nhiều vùng canh tác. Ví dụ, ở châu Á, sự xuất hiện của nó thường làm giảm năng suất hàng năm từ 10 đến 20%, với sự thất mùa hơn 50% khi dịch hại bùng phát.
Không có đủ gen tự vệ hiệu quả trong cải tiến giống đậu nành kháng sâu xanh da láng như vậy. Nghiên cứu này mô tả tiến trình dòng hóa và định tính mộtgen phòng vệ chủ lực, GmMYC3, trong cây đậu nành kháng sâu CCW. Phân tích Omics cho kết quả là gen GmMYC3 có ảnh hưởng đến nhiều gen liên quan đến tự vệ và liên quan đến các chất biến dưỡng, như trypsin inhibitors của đậu nành. Kết quả nghiên cứu xác định GmMYC3 là một nguồn vật liệu di truyền triển vọng cho cải tiến giống với kết quả làm tăng tính kháng sâu CCW.
Sâu ăn lá làm hủy diệt sản lượng cây trồng trên toàn cầu. Phản ứng của cây bị kích hoạt khi bị sấu tấn công làm khởi động tính kháng; do đó, định tính được cơ chế nào liên quan đến tính kháng của cây chủ là cực kỳ quan trọng. Tuy nhiên, thành phần di truyền của tính kháng như vậy đối với sâu ăn lá đậu nành vẫn còn mù mờ. Ở đây, một bgen tự vệ chủ lực, GmMYC3, được phân lập thông qua bản đồ di truyền liên kết (linkage) và bản đồ di truyền association. GmMYC3 mã hóa protein yếu tố phiên mã MYC2, protein này nhanh cóng hoạt động sau khi xử lý jasmonic acid hoặc sau khi bị sâu cắn phá, liên quan đến kết quả kháng sâu hại chính, sâu CCW, trong cây đậu nành. GmMYC3 tích cực điều tiết nhiều gen liên quan đến stress sinh học, giữa những GmMYC3 triggers với biểu hiện cao chất Kunitz-type trypsin inhibitors bên cạnh sự tương đồng của GmMYC1 và vùng downstream của gen GmWRKY56. Sự biểu hiện mạnh mẽ gen GmMYC3 làm tích tụ rất lớn trypsin inhibitors ở lá đậu nành, can thiệp vào sự tiêu hóa protein và chức năng hấp thu của sâu non ăn lá, làm chậm lại quá trình trưởng thành của sâu và nhộng CCW. Kết quả quan sát trên ruộng trồng đậu nành transgenic xác nhận vai trò phòng vệ của gen GmMYC3. Kết quả nghiên cứu di truyền quần thể và di truyền tiến hóa cho thấy haplotype ưu việt của gen GmMYC3 góp phần vào tính kháng sâu CCW mà không làm giảm đáng kể năng suất hạt và chất lượng hạt đậu nành. Chú ý, haplotype này xuất hiện ở tần suất thấp trong nguồn vật liệu giống đậu nành được thuần hóa (giống bản địa). Kết quả làm sáng tỏ hơn cơ chế phân tử của tính kháng cây đậu với sâu CCW và cung cấp nguồn vật liệu đáng giá phục vụ cải tiến giống đậu nành cao sản kháng sâu.
Xem https://www.pnas.org/doi/10.1073/pnas.2424956122
Bộ chỉ thị phân tử cực lớn “1K-core” phục vụ quản lý nguồn gen hoang dại và tạo vật liệu ban đầu cho cải tiến giống lúa từ nguồn lúa hoang
Nguồn: Debashree Dalai, Dipti Ranjan Pani, Swayamsiddha Aswita Dhal, Motilal Behera, Tapan Kumar Mondal, Muhammad Azaharudheen TP, Joshitha Vijayan, Deepa Sarkar, Pallavi Ghose, Abhijeet Roy, Kutubuddin A Molla, Anilkumar C, Lotan Kumar Bose, Trilochan Mohapatra, Soham Ray, Meera Kumari Kar & Mridul Chakraborti. 2026. A robust 1K-core marker set for wild germplasm management and targeted pre-breeding of rice: development and applications. TAG; January 3 2026; vol. 139; article 23
Bộ chỉ thị phân tử STMS (sequence tagged microsatellite sites) phục vụ cho nghiên cứu Oryza sativa complex đã được phát triển, được minh chứng và được sử dụng phục vụ pre-breding cũng như định tính ngân hàng chi Oryza từ những taxa khác nhau.
Phát triển có tính chất toàn bộ hệ gen (genome-wide) những markers chuyển giao chéo đã được phân phối; kết quả này ứng dụng cho nhiều loài khác; có thể tăng cường hiệu qua nguồn vật liệu pre-breeding. Sàng lọc tất cả 23.5K primer pairs thông qua chín hệ gen tham chiếu đã xác định được 1.008 chỉ thị STMS có khả năng khuếch đại, bao gồm 520 genic ones, đối với Oryza sativa complex.
![]()

Hình: Oryza rufipogon ở Tràm Chim (BCB photo)
Độ dài khuếch đại dự đoán của những markers này được làm rõ thông qua PCR. Bên cạnh đó, có 3.628–13.280 markers được người ta xác định phục vụ từng loài riêng biệt. Hầu hết markers có tính chất cross-amplifiable đều có tính chất syntenic trong genome AA. Tuy nhiên, sự chuyển vị có tính chất intra- và inter-chromosomal (giữa và trong nhiễm sắc thể) đã dược tìm thấy trong loài hoang dại O. longistaminata, O. nivara, và O. meridionalis so với loài có genome AA khác cũng như các subspecies. Chú ý, bốn markers biểu hiện sự chuyển vị giữa các nhiễm sắc thể trái ngược nhau, giữa 3 loài genome AA ở châu Á và 5 loài lúa hoang khác của châu Phi, Nam Mỹ, châu Úc. Trong bộ chỉ thị “1K cross-amplifiable core markers”, có 629 STMS loci có tính chất syntenic được người ta xem như là kết quả của “cross-transferable” giữa những loài genome AA, có 3 markers cho thấy độ dài khuếch đại khác biệt nhau rõ ràng giữa loài khác nhau. Bên cạnh đó, có 42 markers được dự đoán là “cross-amplifiable” giữa O. sativa complex, O. punctata, và O. coarctata. Sự khuếch đại giao thoa ấy trên cơ sở chạy PCR của markers trong 21 loài của chi Oryza biểu thị chiều dài khuếch đại có tính chất “hyper-variable”, cho dù bản chất synteny của chúng có thể chưa được khẳng định. Những markers của genome AA, giữa những loài lúa hoang biểu thị markers có tính chất “combination-wise” (kết hợp khôn ngoan), cung cấp một nguồn genomic đáng tin cậy phục vụ phát triển các dòng lúa CSSLs (chromosome segment substitution lines), bản đồ di truyền, và du nhập tính trạng đa dạng từ loài lúa hoang sang loài lúa trồng, kể cà O. sativa, O. glaberrima, và giống lúa mới phục vụ châu Phi (NERICA). Những markers được chọn ấy được sử dụng để phát triển quần thể con lai CSSLs du nhập tính trạng của lúa hoang O. rufipogon vào nền di truyền lúa trồng O. sativa.
Xem https://link.springer.com/article/10.1007/s00122-025-05133-1
Chỉnh sửa gen nhờ hệ thống CRISPR/Cas9 thông qua promoter chuyên dụng trên mô sẹo pYCE1 của hệ gen cây sắn (Manihot esculenta Crantz)
Nguồn: Yuanchao Li, Ruxue Bao, Mengtao Li, Changying Zeng, Haojie Yang, Yuan Yao, Youzhi Li , Wenquan Wang, Xin Chen. 2025. Improving gene editing of CRISPR/Cas9 using the callus-specific promoter pYCE1 in cassava (Manihot esculenta Crantz). Front Plant Sci.; 2025 May 20: 16:1600438. doi: 10.3389/fpls.2025.1600438.

Những nghiên cứu trước đây cho thấy có một promoter tương ướng có thể điều khiển Cas9 transcription trong hệ thổng chỉnh sửa gen CRISPR/Cas9, mà hệ thống này cải tiến được hiệu quả của công nghệ chỉnh sử hệ gen hoặc gen đích. Ở đây, người ta xác định và định tính được promoters chuyên biệt cho mô sẹo nhằm tăng cường hiệu quả của chỉnh sửa gen trong hệ gen cây sắn. Từ cơ sở dữ liệu transcriptome của 11 mô tế bào sắn, gen có tên YCE1 được phân lập chỉ biểu hiện trên mô sẹo nào đó mà thôi. Promoter của nó (pYCE1) có thể tá động một cách hiệu quả và chuyên biệt tiến trìn phiên mã EGFP trong mô sẹo. Như vậy mô sẹo dễ vỡ từ phát sinh tế bào phôi (FECs) là đơn vị nhận phục vụ chuyển nạp gen của cây sắn, người ta thay thế promoter gốc 35S bằng pYCE1 chạy tới phiên mã Cas9 nhằm cải tiến hệ thống CRISPR/Cas9. Trong chỉnh sửa một gen đơn nào đó, tỷ lệ đột biến chủ đích tăng đáng kể, nó đạt tỷ lệ đột biến tổng thể là 95,24% và đột biến đồng hợp tử 52,38%, so với con số 62,07% và 37,93% với 35S promoter, theo thứ tự. Hơn nữa, đạt được đột biến đồng hợp tử hai gen là 64,71% trong chỉnh sửa hai gen chứng minh rằng có một hiệu quả rất cao của pYCE1 trong ứng dụng công nghệ chỉnh sửa gen cây sắn. Kết quả này nhấn mạn tiềm năng của pYCE1 làm tăng cường hiệu quả chỉnh sửa gen theo hệ thống CRISPR/Cas9 trong cây sắn. Cách tiếp cận này mở được cho nghiên cứu chức năng gen và cải tiến giống sắn.
Xem https://pubmed.ncbi.nlm.nih.gov/40464017/
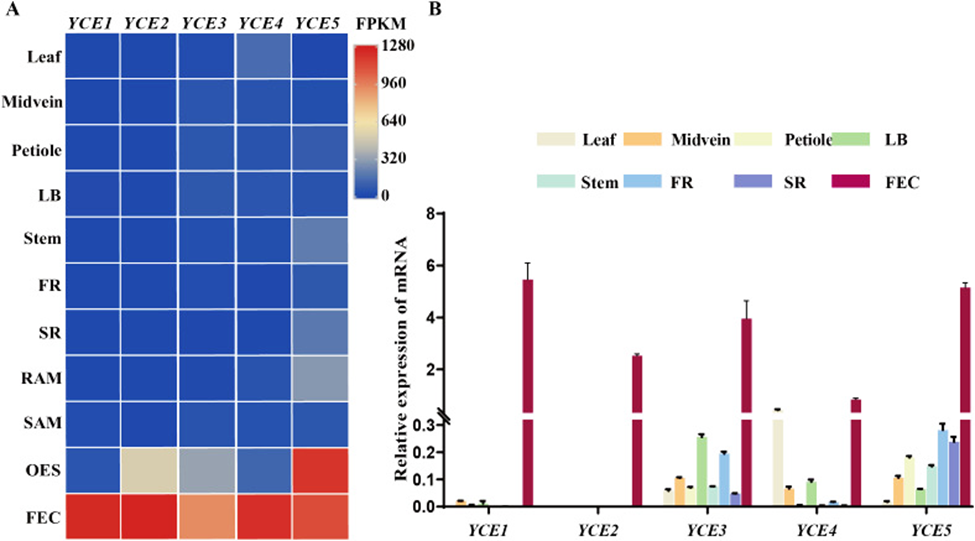
Xác định gen đặc biệt cho từng mô sẹo. (A) Gen ứng cử viên biểu hiện mạnh mẽ trong mô sẹo. LB, lateral bud (chồi mọc ngang); FR, fibrous root (rễ xơ); SR, storage root (rễ dự trữ); RAM, root apical meristem (sinh mô ngọn rễ); SAM, shoot apical meristem (sinh mô ngọn của chồi); OES, organized embryogenic structures (kiến trúc phôi có tổ chức tốt); FEC, friable embryogenic callus (mô sẹo sinh phôi). (B) Minh chứng gen biểu hiện mạnh và chuyên tính với mô sẹo theo kết quả RT-qPCR.
Số lần xem: 104













